Målrettet RNA nedbrydning
I samarbejde med to andre europæiske grupper har forskere fra Aarhus Universitet afdækket de molekylære detaljer, der fører til målrettet rekruttering af det vigtige nedbrydningsmaskineri, RNA exosomet, til dets nukleare RNA substrater. Fremtidige undersøgelser kan nu afdække, om denne RNA nedbrydningsvej er kritisk under embryonal udvikling, celledifferentiering og forskellige former for stress.
Nuklear RNA omsætning
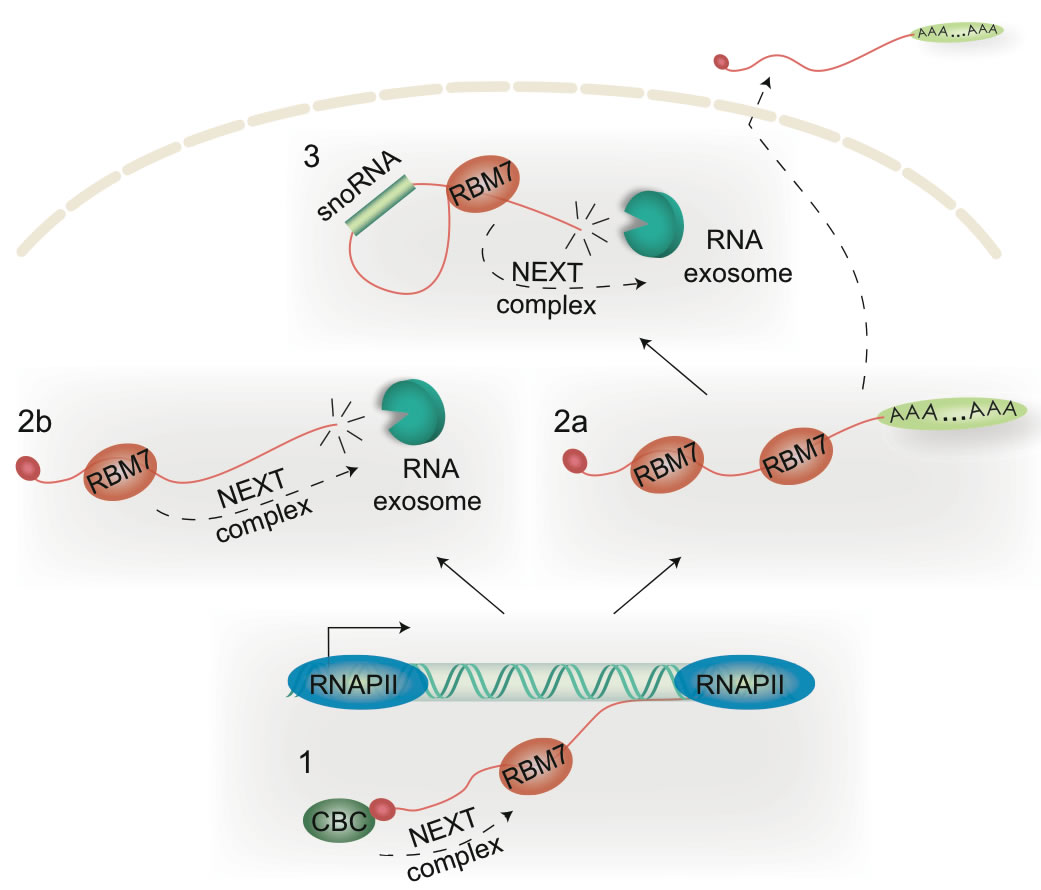
I cellekernen er det RNA exosomets aktivitet, der bestemmer. Derfor er nukleare RNA'er normalt godt beskyttede af bundne proteiner, hvilket også betyder, at der er behov for et sæt exosome adaptorer for at opnå specificitet, således at kun uønskede molekyler fjernes. En sådan målretning af RNA exosomet er velbeskrevet i gærceller, men hvor godt systemet er bevaret gennem udviklingen til menneskets celler har været uvist.
NEXT komplekset og dets mange substrater
Michal Lubas, postdoc i Torben Heick Jensens gruppe, opdagede i 2011 sammen med sine samarbejdspartnere det såkaldte Nuclear EXosome Targeting (NEXT) kompleks som en aktivator for det nukleare exosome i humane celler. NEXT komplekset huser RNA-helicasen hMTR4, zink-”knuckle” proteinet ZCCHC8 og det RNA-bindende protein RBM7. Nyere undersøgelser fra samme forskningsgruppe har vist, at NEXT exosome-aksen tjener til at undertrykke den udbredte (pervasive) aktivitet af det menneskelige genom. Med udgangspunkt i denne opdagelse har Aarhus-forskerne nu forsøgt at beskrive, hvorledes den molekylære genkendelse af RNA finder sted ved hjælp af NEXT, og hvordan dette fører til RNA-nedbrydning.
Karakterisering af cellulære NEXT-RNA interaktioner
Ved at bruge en ” transcriptome -wide” in vivo RNA-interaktions metode, den såkaldte iCLIP teknologi, som fremgangsmåde påviste nærværende analyse en stor mængde NEXT-bundne RNA substrater. Konsistent med NEXT’s rolle i hurtig nedbrydning af RNA har mange af disse en kort livscyklus, for eksempel ”enhancer” RNA’er (eRNA’er), PROMoter uPstream Transcripts (PROMPTs), lange non-coding (ikke-kodende) RNA’er (lncRNA’er) samt metabolitter af små nukleare RNA-molekyler (nucleolar (sno)RNA’er).
Det er dog interessant at bemærke, at NEXT-binding i sig selv ikke automatisk fører til RNA nedbrydning. I stedet ”tilbyder” tilstedeværelsen af NEXT en mulighed for exosomal nedbrydning, hvilket kun sker, hvis en tilstedeværende RNA 3'ende er ubeskyttet. Denne form for NEXT-medieret RNA nedbrydning forekommer at være en enkel og effektiv måde at udføre nuklear RNA-kvalitetskontrol uden en forudgående, og kompliceret, RNA sorteringsmekanisme.
Arbejdet, som netop er offentliggjort i open access tidsskriftet Cell Reports, blev udført af postdocs Michal Lubas og Peter Refsing Andersen fra Torben Heick Jensens gruppe ved Danmarks Grundforskningsfonds ”Centre for mRNP Biogenesis and Metabolism”, Institut Molekylærbiologi og Genetik, Aarhus Universitet. Projektet var udført i samarbejde med Grzegorz Kudlas forskningsgruppe ved University of Edinburgh og Andrzej Dziembowskis gruppe ved University of Warsaw.
Link til den videnskabelige artikel i Cell Reports.
Mere information
Professor Torben Heick Jensen
Center for mRNP Biogenese and Metabolisme
Institut for Molekylærbiologi og Genetik
Aarhus Universitet
6020 2705, thj@mbg.au.dk
