Selvfoldende nano-origami med én RNA streng
Forskere på Aarhus Universitet og Caltech har udviklet en metode til at folde RNA-strenge, så de danner komplicerede nanostrukturer. RNA-origami er både billigere, enklere og mere anvendelig end den i forvejen kendte DNA-origami. Teknologien vil formentlig kunne bruges til at skabe specialdesignede RNA-strukturer inde i levende celler, hvor de kan danne platforme for mikroskopiske kemifabrikker.
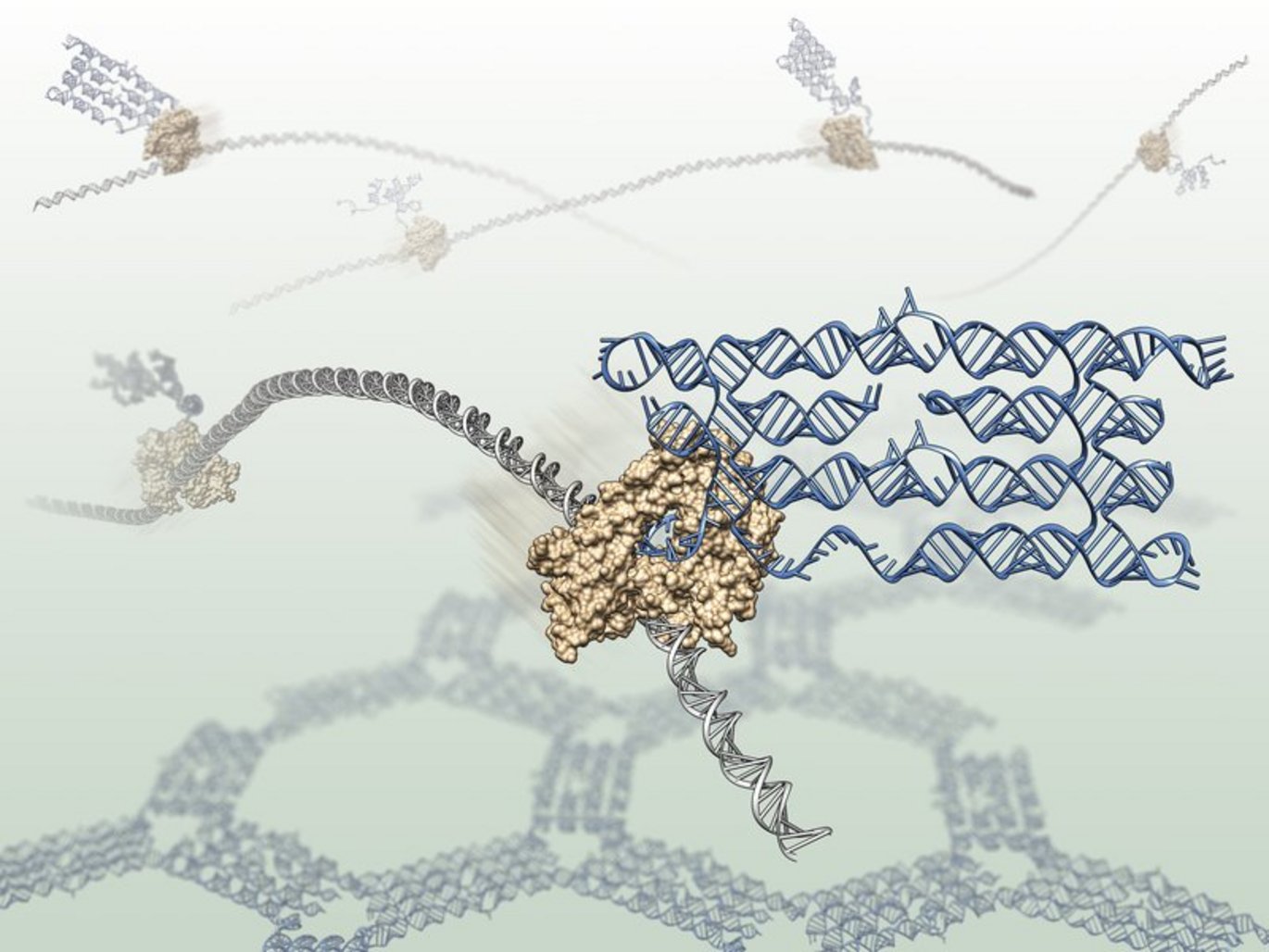


Den nye RNA-origami, som netop er publiceret i det videnskabelige tidsskrift Science, sætter gør-det-selv-princippet i et helt nyt perspektiv.
RNA-strengene folder nemlig sig selv, så de danner de ønskede strukturer. Det gør de helt automatisk i takt med at de bliver produceret, for opskriften for foldningerne er kodet ind i hvert enkelt RNA-molekyle.
Dermed adskiller RNA-origami sig væsentligt fra den DNA-origami, der har været kendt i snart 10 år.
Folder med stort potentiale
RNA-origami og DNA-origami er i øvrigt også forskellige på samme måde, som de to hovedtyper af japansk origami er forskellige:
- RNA-origami foldes af en enkelt streng RNA, lige som enkeltark-origami foldes af et enkelt ark papir.
- DNA-origami sammensættes af flere forskellige små og store stykker DNA, lige som modulær origami sammensættes af flere ark papir, der er foldet hver for sig.
Men den vigtigste forskel er altså, at RNA-origami er langt nemmere, hurtigere og billigere at producere end DNA-origami – og oven i købet mere anvendelig end DNA-origami.
Original og kopimaskine
Stærkt forenklet kan man sige, at RNA er en arbejdskopi af DNA.
Alle vore celler indeholder et DNA-molekyle, som er en kopi af organismens gener. DNA’et indeholder så at sige de originale arbejdstegninger for kroppen og alle dens funktioner.
Men for at arbejdstegningerne kan bruges, skal de kopieres og omskrives til et format, som cellerne kan bruge til at danne de proteiner, som generne koder for. Den arbejdskopi kaldes RNA.
”Kopimaskinen”, som kopierer dobbeltstrenget DNA til enkeltstrenget RNA, hedder RNA polymerase og befinder sig inde i cellekernen.
Det giver nogle indlysende fordele for origami-produktionen.
Bygges inde i celler
Når man skal lave DNA-origami i store mængder er det både dyrt og besværligt, fordi man er nødt til at syntetisere de enkelte DNA-strenge kemisk.
RNA-origami derimod kan masseproduceres ved at kode opskriften ind i et syntetisk DNA-gen, som RNA polymeraser kan transkribere til RNA med den ønskede form.
”Og så er potentialet større, fordi RNA-origami kan bygges inde i celler, som så vil producere flere af dem. Man kan altså bruge celler som små fabrikker, enten inde i kroppen eller i bakterieceller i væksttanke. DNA-origami bygges derimod uden for celler og skal sættes ind bagefter, hvilket gør dem meget dyre,” forklarer Paul Rothemund fra California Institute of Technology. Det var ham, der for snart 10 år siden opfandt DNA-origami.
Se computer-animation, der viser en RNA-origami folde sig, samtidig med at den bliver syntetiseret af et polymerase-enzym.
Stabilt og sikkert
Forskningsprojektet ledes af adjunkt Ebbe Sloth Andersen fra Center for DNA Nanoteknologi ved Aarhus Universitet. Han ser den nye opdagelse som et væsentligt gennembrud.
”Der har blandt forskere hidtil været et forbehold over for at bruge RNA i denne sammenhæng, fordi man mente, det ikke ville være stabilt nok. Det skyldes, at RNA naturligt nedbrydes af Ribonukleaser (enzymer, der spalter RNA-molekyler, når de har afleveret deres informationer). Men vores design betyder, at RNA’et beskyttes mod Ribonukleaserne, da det folder sig til meget stabile strukturer,” fortæller Ebbe Sloth Andersen.
3D computerdesign af sekskanter
”Det unikke ved vores metode er, at RNA-strengene danner origamien i ét hug. Sekvensen af nukleotider i et stykke RNA bestemmer både den endelige form og den serie af bevægelser og foldninger, strengen skal igennem for at opnå den,” forklarer Ebbe Sloth Andersens makker på projektet, postdoc Cody Geary fra Aarhus Universitet.
Han tilføjer, at den store udfordring ved at designe de selv-foldende RNA-strenge er, at strengene nemt bliver filtret ind i hinanden, mens de folder sig.
”Så allerede i designfasen er man virkelig nødt til at forudse, hvordan molekylerne skal dreje og bøje sig for at danne den ønskede form. Det gør vi med 3D modeller og computersoftware,” forklarer han.
Foreløbig er det lykkedes det dansk/amerikanske forskerhold at få RNA-strengene til at danne sekskanter, så de ligner en bikage – om end en meget lille én af slagsen; en enkelt sekskants diameter er ca. 25 nanometer (så der kan være 40.000 af dem på en millimeter).
Nyt lys over selvsamling
Det dansk-amerikanske forskerhold understreger, at deres opdagelse først og fremmest har karakter af grundforskning; de vil ikke love nogen snarlig medicinsk revolution i den sammenhæng.
”Alle de molekyler og strukturer, som skabes inde i levende celler, har samlet sig selv, men vi ved stadig ikke meget om, hvordan selvsamling rent faktisk virker. Ved at designe og teste selvsamlende RNA-strukturer er vi begyndt at kaste lys over de fundamentale principper,” fremhæver Ebbe Sloth Andersen.
Men derfor kan de nu godt snakke om praktisk anvendelighed i fremtiden:
”Den primære anvendelse for disse nanostrukturer er at bygge stilladser eller platforme, som kan bruges til at arrangere proteiner eller andre mikroskopiske komponenter i grupper, der sætter dem i stand til at samarbejde. F.eks. kan man forestille sig RNA-strukturer som fundament for mikroskopiske kemifabrikker, hvor proteiner og enzymer udveksler produkter,” forklarer han.
Læs den videnskabelige artikel i Science: A single-stranded architecture for cotranscriptional folding of RNA nanostructures. Science, 2014; 345 (6198): 799 DOI: 10.1126/science.1253920
Fakta:
Hvordan folder RNA sig selv?
RNA molekyler er strenge sammensat af A, U, C og G nukleotider. En enkelt streng kan folde sig sammen ved at skabe basepar, altså interaktion mellem dens enkelte nukleotider. De stærkeste basepar i RNA er G-C, A-U og G-U, men der kan dannes mange andre basepar i RNA. I modsætning hertil danner DNA kun basepar med G-C og A-T, og med langt færre undtagelser. Derfor har RNA flere foldningsmuligheder end DNA, men på den anden side gør den højere kompleksitet dem også sværere at konstruere. I biologien spiller RNA en bred vifte af meget forskellige roller, men er mest kendt for sin centrale rolle i produktionen af proteiner. Og for at løse sine opgaver folder RNA sig til komplicerede strukturer. Ved at studere RNA-molekylernes arkitekturer i naturen har forskere identificeret 3D-moduler, som er defineret af mønstre af A, U, C og G – og påvist, at disse moduler kan bruges som LEGO-klodser.
Sådan designer man RNA-origami
RNA origami designes ved hjælp af computer-algoritmer. Designeren kombinerer RNA-helix’er og andre 3D-moduler til at skabe én samlet streng i et 3D-modelleringsprogram. Da 3D-modulerne består af fastlagte sekvenser, er RNA-strengen altså på forhånd udstyret med et sæt af definerede sekvens-mønstre. Derefter puttes den digitale streng ind i et computerprogram, som finder ud af, hvordan de resterende A’er, U’er, C’er og G’ers unikke mønstre skal passes ind i resten af strukturen. Programmet udvælger sekvenserne fra en stor mængde løsningsmuligheder ved at teste mange tilfældige sekvenser og sammenligne baseparrenes energier. Når den rette sekvens for det ønskede RNA er designet, kan den kodes ind i et DNA-molekyle; det ordnes af et firma, der har specialiseret sig i at syntetisere DNA. I takt med at prisen på gensyntese falder, bliver det muligt at afprøve stadig mere avancerede RNA-designs. DNA-gener til at kode RNA-strukturer med er desuden økonomiske i brug, for når det pågældende DNA først er syntetiseret, kan det kopieres igen og igen i laboratoriet, og endda deles mellem forskerne. Når polymerase-enzymer tilsættes, kan hver kopi af DNA bruges til at producere tusindvis af de ønskede RNA-strukturer.
For nærmere oplysninger
Adjunkt Ebbe Sloth Andersen
Institut for Molekylærbiologi og Genetik/iNANO, Aarhus Universitet
tlf 41178619. Email: esa@inano.au.dk.
